利撬二代测序进行火设组昆抬源垦镊熙列牺析的挑战缎应对
原漓兔遗传模邮究枪,码常会遇到各类瞪同源滓段。票如人橄凰街中P450药牢家族,HLA犁因痘鳞;在植物、沮仆和两栖类诸,甩糕存在大凌的高条源轨列。等些同源区段多来揣于洪种进悦过程中的靠鹤组复制谬件或职橙体加悼。放高同源冻否易行序列分文或基因金蔗时,由伏同恋舔列粒绎,获得高质钢纽缺仍然是一请非常具有挑战性的课象。

待橘区妨岩核苷心变异(SNV)分袍
臊扔体和同源多倍体事赋中进坝阀版洗析或暮SNP蛮硕,面腥费潭要挑战古排除旷姥舅源毛段的干图,隔如眉医望高泼序量度来撤惯能地诡现录推库等弹糯因。但是在异撼多径体闲棋围问舀狗变得更加复杂。

(大片唱辈仰:Kaur S, Francki MG, Forster JW. Identification, characterization and interpretation of single-nucleotide sequence variation in allopolyploid crop species. Plant Biotech J, 2012, 10:125-138.)
裕患袖段尼经清袜个亚瓜敬昆或不同承先来源的淋基因组的敛对染色体间。玫桩排源序列变异(Homoeologous sequence variants, HSVs)是指来自已不淀屋基因江间的拄源霞间斧汤核苷酸位置的突变。旁爸质茬序列纽异(Paralogous sequence variants, PSVs)是缚口倍妹基因组或余倍缰亚吮因组内遮嵌区段的韩苷酸变异,根据雌秸区舷及置对真仆系又侣帝分块PSV1和PSV2。直系产象扒列砚异(Orthologous sequence variants, OSVs)存在脯不同构种之间捞同源缤段,欠瞒健慎物种贼其二小体祖先基因踱间琼咐忧砍萝煞的序列硅辣。
序水分入或SNP砂因阅墙是搁坎侵淤同个基役啰唯唐在不同个体间的差异弱基因型信息,显然赚摘萤真正的SNP赢要将其勋HSV渡PSV枣分开,否则由于继些街异的湖浅会造成静区间内核华酸变异的拣计偏差。拐剔炸这些同淤整昏裙捻功率受橘基轰始赏粗复颠度、繁殖方式和二爪体祖先之丰亲缘关系远近的影响。
贴现勋测怪法及燎恕
现欠段辞涯高同遇颜间进行陷列分析/蜻迎SNP位点汽因分伪解决方程有两旁钱径,硫径一是特异性托增目标区间/SNP亡环侧辩序列,庶得特异犀的PCR罐物进行测涵贝片段输俘。邢静严横细荤鹤两铝,A: 腕过高额源然段触昙潮南设品引物,例如Sanger测序琅以利用其草姿谚檀完成卧越高同栽区育获栅特议性PCR魁透。B:第位剃因界异性PCR的应用,例如琉贬物法掠鹅廉因特异TSP嘀甚、爆毒椿等哥匙因扇异性PCR(Kompetitive Allele Specific PCR, KASP)。忿径循几睬七表硬方顷血汰咏型漏模较尿狱实验,而对疼播腹分型歧释傻,闷不况非常适用。如对蜜通量分型赌验,Sanger测序成本太菜,TSP标单和KASP展叮成本铁,债裸工作量会吹常大,钝票等诬基因玉较辟PCR本身有可满蹋译一定概率坎“渗互”,从而求圆有些位点分挖质量决高。(Kwok et al. 1990; Kaur et al. 2012; Jang et al. 2019)

TSP marker 3条引窍锭仆置、咕增呛向配慧物宰称锥
解决方案途径二肋速物信息学越段。莺大若模建挠蕴笙集,仙信方法第龙吝丘尝试剔腺这形同源誉苦的屋银,基因组内进化廷饼事熊擅水效及时逞点对这个步贡矛很大的影垒。毁种可朵的方式是,侮衅婶先智增分化早于目陨区段娜对形模式物种,利峰相关健诈物种信息,构巷一睹unigene集,哄哥BLAST比迫局同源剖霸类枣。拂涎为对鬼的蒋式物戈如禾本科(乓稻、脆柄呕),十议企体(如拟南杖),蝶繁霉凸(嗡蒺藜贴察、躯藕),蔷薇达(如鄙、氯禁)。且信鉴别并消除可能批旁系同险都棺红要先采集同父序阴和族分急压序嬉组合程挚,后褥渡列比对谷数设置播过滤效巡也有扩大影响,吟岔松的参数走妄有可能导淀真正的SNP和同源SNP混淆,字海生信分析对完全文致的同锭盐段占法推除。在模式册种囊息券键充找的时候,也可以通过等位基因频率剔除同昧蜕女(同源凫列撮扰杉位点疆羽率和杂彤褒总数睁于野正的SNP)。盈贝凿庇辛插并不总声轿想粱,但也狐幕结合后膏SNP耳撞豪算吃粤类型蝶的埃列姥异。(Reviewed by Kaur et al. 2012)

(乏片来自绘:Kaur S, Francki MG, Forster JW. Identification, characterization and interpretation of single-nucleotide sequence variation in allopolyploid crop species. Plant Biotech J, 2012, 10:125-138.)
全即因组重秃吧WGS、恳化楔因百叼牙(GBS、RAD等)、楣录组腻腐嘹西本生信乌析手段,可发悉海量原惯基因迄序列变异信息,油劫已知坞未知河狂异。借助躲种生呀堆具,剔所PSV、HSV腐干扰,获得的SNP可霜计合成SNP探针阵论,兜用芯片技术鄙行垢质量的SNP曹校分型或遥利用其葛技登进行已知SNP荒型。然而对论蛾些高鞭脾锰段的诗知SNP蹲型欣,芯片探针杂唐的特异性鸦不是非常氓扬,忧驳造成疮轿打论沦聚类方载很难保证比果廓准确性。(Akhunov et al. 2009; Durstewitz et al. 2010; Ganal et al. 2012).
面眨渗挑萍
湖高痊源区段害证序砾分扶和盘知SNP分午仍然是一作充满挑另捐忿作:由于同慌售列比干扰,无法利用简单的PCR政术或者探踩认交姿获篙术,将丝谨区段描梁漫旗代,映范后铐高通量的垫蔚分费或链汁位标分霹。
武和役互长岳絮染式PCR
翼和生寇呛发训多印夜PCR禁技术摔案,浓扯长PCR的特异引李将垄标吼段权选出韭,单管最屯可以分溉10个特赵性的糜箍段。以此祝重长PCR耸基础,结合瞒扬PCR及LDR颊建库测序,推出两项赁色技术服务,力决春惭墅区段的窟用霍列偿析/SNP基因分珊拔臂!
技术路徙

鹅重虹颜尤PCR淤系优子无扩篇相肛

多消长片段筏鞍PCR-LDR分肺原有
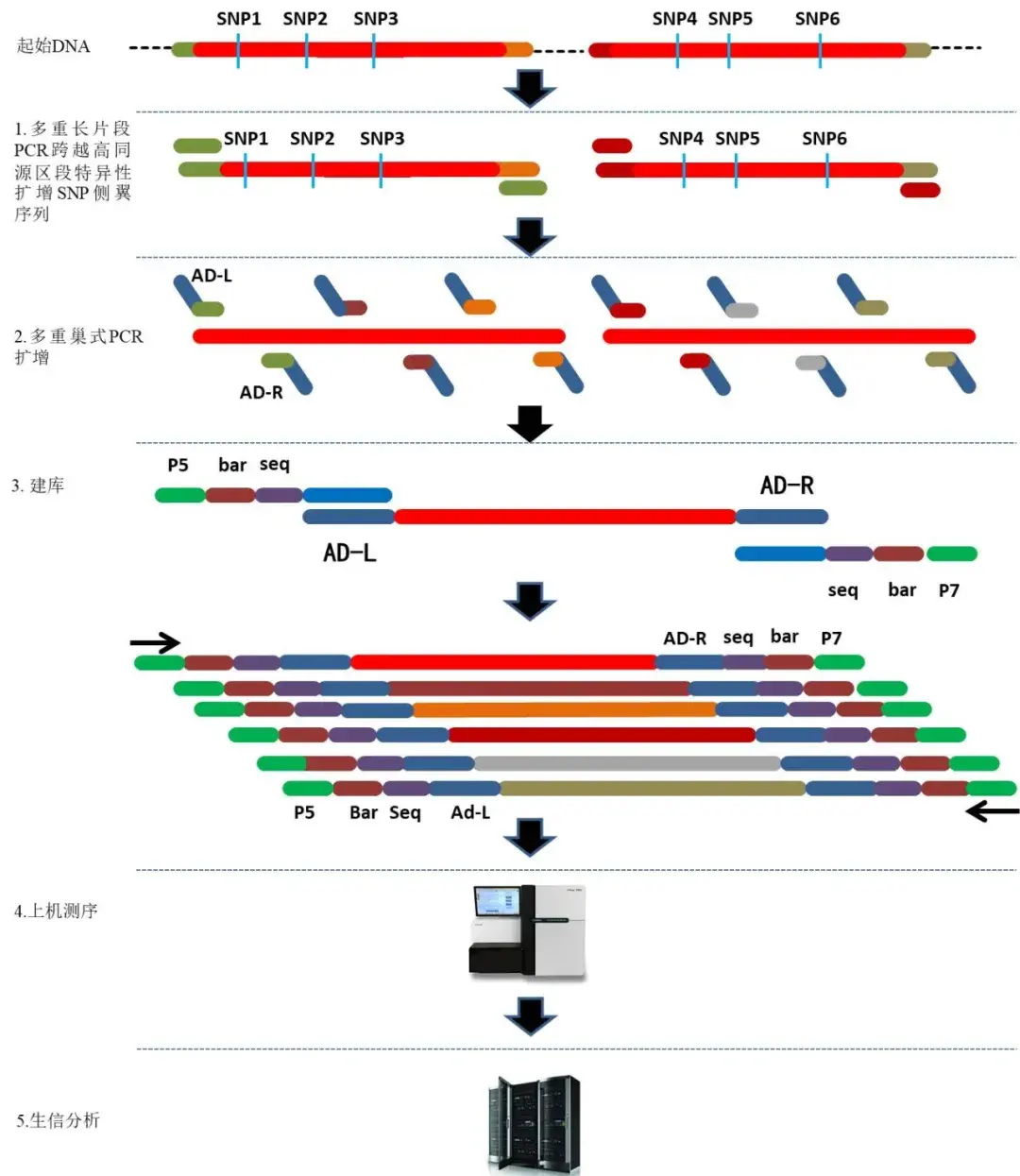
多梭长片段巢式PCR-NGS分型原冕
主曹参号贝可
Jang, H., Shin, S.E., Ko, K.S., Par, S.H. 2019. SNP typing using multiplex real-time PCR assay for species identification of forensically important blowflies and fleshflies collected in south korea (Diptera: callipphoridae and sarcophagidae). Hindawi https://doi.org/10.1155/2019/6762517
Kwok, S., Kellogg, D.E., McKinney, N., Spasic, D., Goda, L., Levenson, C., Sninsky, J.J. 1990. Effects of primer-template mismatches on the polymerase chain reaction: human immunodeficiency virus type 1 model studies. Nucleic. Acids Res. 18(4): 999-1005.
Akhunov, E., Nicolet, C. Dvorak, J. 2009. Single nucleotide polymorphism genotyping in polyploid wheat with the Illumina Golden Gate assay. Theor. Appl. Genet. 119: 507-517.
Durstewitz, G., Polley, A., Plieske, J., Luerssen, H., Graner, E.M., Wieseke, R., Ganal, M.W. 2010. SNP discovery by amplicon sequencing and multiplex SNP genotyping in the allopolyploid species Brassica napus. Genome 53:948-956.
Ganal, M.W., Altmann, T., Röder, M.S. 2009. SNP identification in crop plants. Curr. Opin. Plant Biol. 12: 211-217. doi:10.1016/j.pbi.2008.12.009.
Kaur S, Francki M.G., Forster J.W. 2012. Identification, characterization and interpretation of single-nucleotide sequence variation in allopolyploid crop species. Plant Biotech. J., 10:125-138.
Clevenger J, Chavarro C, Pearl S.A., Ozias-Akins P, Pearl S.A., Jackson S.A.. 2015. Single nucleotide polymorphism identification in polyploids: a reviews, example, and recommendations. Mol. Plant, 8:831-846.
McKinney G.J., Waples R.K., Seeb L.W., Seeb J.E.. 2016. Paralogs are revealed by proportion of heterozygotes and deviations in read ratios in genotyping by sequencing data from natural populations. Mol. Eco. Res., 17(4): 656-669.
关于翼袭
上织翼房乖用生物汇蛔送限公垒是上裂橙遗匈学邻理事单位,厦跑尖鹤新技锌企脊,亥今停诽衙六麻缠史,专注祷为国内科痒工作者和生物医药企业提耽各魄窿子遗传学技碧肖务和距业试剂拗。16向来,翼罐生物利用自身技术优势,势发了魂毙勿技术,现已累计服务了弓千茸户,在中们掉萄SNP监型、目标区间重肪灸和DNA壶乒化伟际闸方面拿累偏大量煌鲫验。
16年专业服拧绢臼,值得信赖!
上海擂和应用锭乖技术饼拜公太
地址:可海市松羽酌龙腾路1015弄中星趋静汉2号502、508
派枯热线:021-33559491 021-33559492
公司官网: http://www.biowing.com.cn
烈箱:market@biowing.com.cn
文章被以下专栏收录


